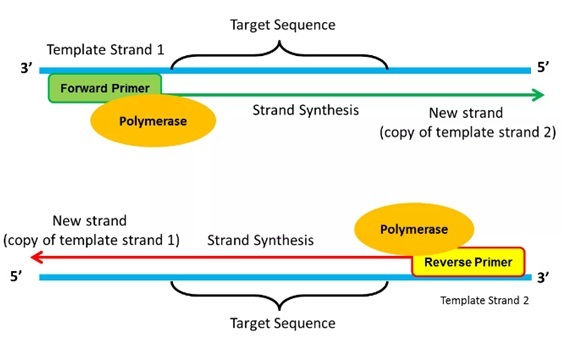
PCR là một trong những phát minh quan trọng nhất của thế kỉ 20. Phản ứng này nhằm sao chép tạo ra một lượng lớn phân tử ADN đích, giúp xác định, và phát hiện các mầm bệnh lây nhiễm như HIV, viêm gan hoặc phát hiện các thay đổi về mặt di truyền như đột biến. PCR được thực hiện thông qua 3 bước: biến tính (denaturing), gắn mồi (annealing), và kéo dài chuỗi (extending). ADN được sử dụng làm khuôn có cấu trúc xoắn kép, khi bị biến tính bởi nhiệt nó tách ra thành 2 mạch đơn, một mạch mang nghĩa (sense) và một mạch đối nghĩa (antisense). Khi nhiệt độ hạ xuống đến nhiệt độ gắn mồi, một mồi sẽ gắn đặc hiệu vào mạch mang nghĩa trong khi một mồi khác sẽ gắn vào mạch đối nghĩa. Trong đó, mồi là các trình tự oligonucleotide ngắn có thể bám đặc hiệu vào một vùng trình tự nhất định. Mồi sẽ là điểm khởi đầu để các polymerase có thể thực hiển tổng hợp mạch bổ sung mới cũng như xác định đoạn ADN được khuếch đại. Do đó, việc thiết kế mồi sẽ quyết định mức độ đặc hiệu và năng suất của phản ứng.
Nguyên tắc thiết kế mồi
1. Độ dài của mồi: Nên nằm trong khoảng từ 15-30 base, độ dài tối ưu là khoảng từ 18-22 base. Điều này phụ thuộc vào việc mồi cần đủ dài để gắn đặc hiệu và đủ ngắn để có thể gắn dễ dàng vào khuôn tại nhiệt độ gắn mồi.
2. Đầu 3’ và 5’ của mồi: Cần thiết kế sao cho đầu 3’ của mồi xuôi sẽ mở rộng về phía mồi ngược và đầu 3’ của mồi ngược sẽ mở rộng về phía mồi xuôi khi được gắn vào 2 mạch bổ sung. Nếu ngược lại thì sản phẩm PCR sẽ không thể được tạo ra.
3. Nhiệt độ nóng chảy của mồi Tm: Điểm nhiệt độ này được định nghĩa là điểm nhiệt mà tại đó 50% sợi đôi ADN phân tách nhau và tạo sợi đơn. Điểm nhiệt này rất quan trọng ở pha gắn mồi, Tm nên nằm trong khoảng 50-65oC. Nhiệt độ nóng của mồi trên 65 độ dễ dẫn đến xu hướng mồi gắn không chính xác. Nhiệt độ Tm của hai mồi không chênh lệch nhau quá 2oC, nhiệt độ chênh lệch quá 5oC có thể không thể tạo ra được sản phẩm. Công thức tính Tm như sau:
- Công thức đơn giản: Tm=4°C x (G + C) + 2°C x (A + T)
- Công thức chứa nồng độ muối: Tm = 81.5 +16.6 x (log10[Na+]) + 0.41 x (%(G+C)) – 675/n
Trong đó: [Na+] là nồng độ phân tử muối, n là số base của mồi.
4. Nhiệt độ gắn mồi (Ta): Được tính dựa vào nhiệt động nóng chảy của mồi. Nhiệt độ gắn mồi thấp có thể dẫn đến lượng sản phẩm PCR được tạo ra thấp, do không đủ số lượng phức hợp lai giữa mồi và khuôn. Ngược lại, sản phẩm không đặc hiệu sẽ được tạo ra nhiều nếu nhiệt độ gắn mồi quá thấp. Người ta thường tính nhiệt độ gắn mồi theo công thức sau:
Ta = 0.3 x Tm(Mồi) + 0.7 Tm (sản phẩm) – 14.9
5. Mật độ GC: Ảnh hưởng đến Tm, do đó mật độ GC nên nằm trong khoảng 50 – 60%.
6. Kẹp GC: Nên có ít nhất một G hoặc C ở đầu 3’ của mồi để giúp cho đầu 3’ của mồi liên kết mạnh hơn. Tuy nhiên nên tránh việc trong 5 base đầu 3’ có nhiều hơn 3 G hoặc C do có thể gây liên kết đầu 3’ quá mạnh khiến mồi bắt cặp không đặc hiệu.
7. Lưu ý cấu trúc bậc 2 trong thiết kế mồi
a) Hình thành hiện tượng kết cặp (dimer): Là hiên tương mồi thay vì gắn vào khuôn sẽ gắn vào mồi ngược với nó hoặc với chính nó, tạo ra các sản phẩm PCR có kích thước nhỏ và làm giảm lượng mồi bắt cặp với khuôn. Do đó cần tránh tạo ra hiện tượng kết cặp
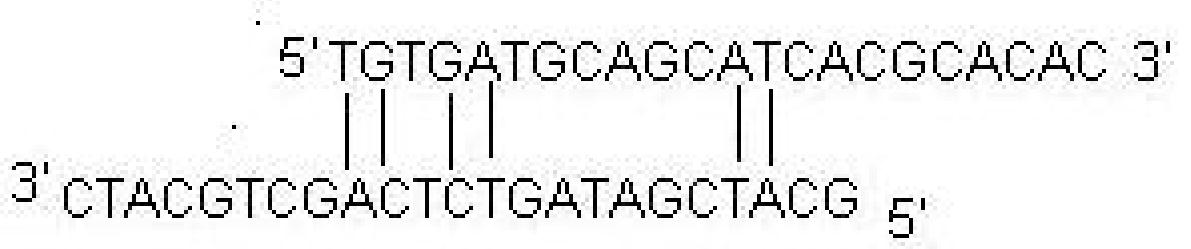
b) Cấu trúc kẹp tóc: có thể được hình thành bởi sự tương tác bên trong chính đoạn mồi. Cần tránh điều này vì làm giảm hiệu quả của phản ứng PCR.
8. Lặp: là hiện tượng lặp lại nhiều lần trong trình tự mồi của trình tự đôi (VD: ATATATATAT) hoặc đơn (VD: GGGGG). Điều này có thể gây bắt cặp nhầm do đó số lần lặp tối đa của một mồi là 4 lần lặp cho cả hai trường hợp.
9. Tương đồng chéo: Là hiện tượng mà cặp mồi sẽ khuếch đại một gene khác có trong hỗn hợp ban đầu. Để tránh hiện tượng này, mồi sau khi thiết kế cần được đưa lên BLAST để so sánh và kiểm tra độ đặc hiệu.
Tuy vậy, việc thiết kế mối khó có thể được thực hiện thủ công vì có quá nhiều thông số phải tính đến. Do đó các nhà tin sinh học đã phát triển rất nhiều phần mềm trợ giúp công việc thiết kế mồi. Phần tiếp theo sẽ hướng dẫn chi tiết cách sử dụng một phần mềm thiết kế mồi phổ biến và miễn phí là Primer-Blast để thiết kế cặp mồi mong muốn. Hơn nữa, bài viết còn giới thiệu và đưa ra sự so sánh giữa một số phần mềm thiết kế mồi khác nhau.
Hướng dẫn sử dụng phần mềm thiết kế mồi Primer – Blast
Primer-BLAST là một công cụ được phát triển bởi NCBI giúp người dùng thiết kế mồi đặc hiệu cho một phản ứng PCR cụ thể. Primer-BLAST sử dụng mã nguồn mở Primer3 để thiết kế mồi, sau đó dùng công cụ BLAST và thuật toán định tuyến tổng quát (global alignment) để kiểm tra trong cơ sở dữ liệu của NCBI nhằm tránh các sai sót kết cặp, tương đồng chéo là nguyên nhân dẫn đến phản ứng PCR không hiệu quả.
Quá trình thiết kế đoạn mồi sử dụng Primer-BLAST thường diễn ra theo 2 bước:
- Thu thập khuôn mẫu
- Thiết kế đoạn mồi
1.1. Thu thập khuôn mẫu
Một ưu điểm khá lớn khi sử dụng Primer-BLAST là người dùng có thể tận dụng tối đa nguồn cơ sở dữ liệu từ NCBI.
Ví dụ sau đây chúng tôi sẽ hướng dẫn thiết kế mồi cho đoạn gen YP_009173871.1 quy định cấu trúc vỏ nhỏ protein của virus viêm gan siêu vi B.
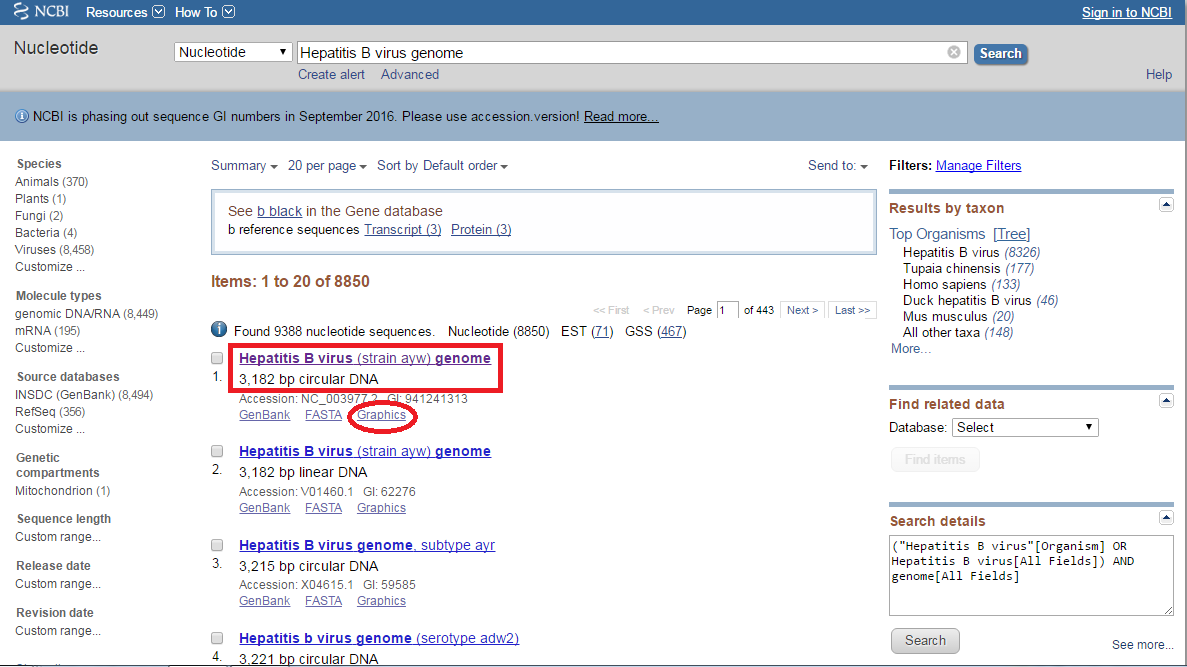
Bước 1: Truy cập cơ sở dữ liệu của NCBI (http://www.ncbi.nlm.nih.gov/) chọn “Nucleotide database” và tìm kiếm sử dụng từ khóa “Hepatitis B virus genome”.
Bước 2: Kết quả trả về là hàng loạt các dữ liệu bộ gen khác nhau của virus viêm gan siêu vi B. Chúng ta sẽ chọn kết quả đầu tiên. Ở phần kết quả số 1 này, sẽ có 3 định dạng là: GenBank, FASTA và Graphics. Để thu chuỗi khuôn mẫu chúng ta có thể chọn FASTA hoặc Graphics nhưng chúng tôi có lời khuyên nên sử dụng Graphics của NCBI thì sẽ hiệu quả hơn rất nhiều. Vì vậy ở mục này chúng ta sẽ chọn Graphics để đánh giá trực quan toàn bộ bộ gen của virus (xem hình 1).
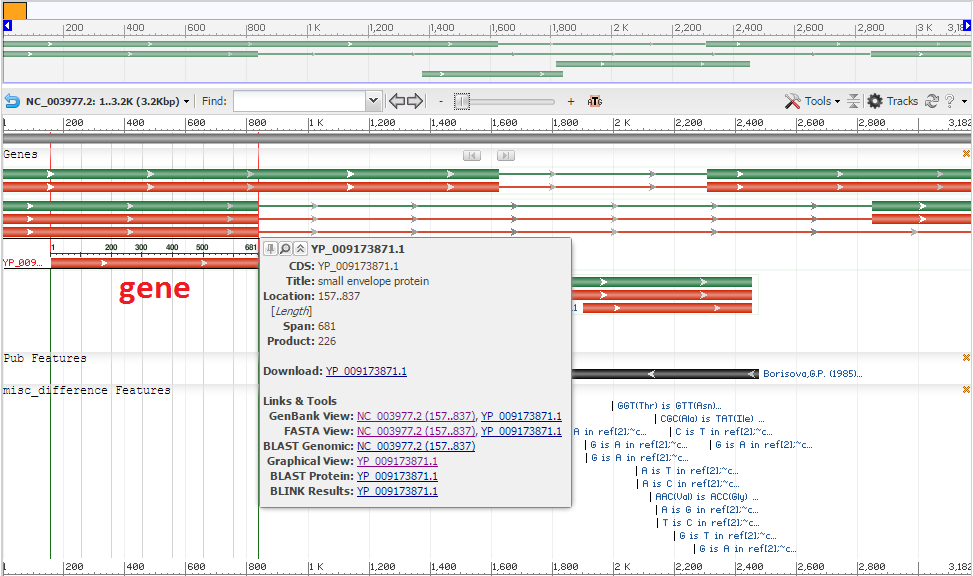
Bước 3: Bộ gen của virus được biểu diễn dưới dạng hình ảnh trực quan (Hình 2). Toàn bộ các gen đều được chú thích và khi click vào từng gen sẽ hiện ra thông tin chi tiết về gen đó.
Trong ví dụ này, chúng ta sẽ chọn gen YP_009173871.1 quy định cấu trúc vỏ nhỏ protein.
Bước 4: Bảng nhỏ hiện lên sau khi chúng ta chọn gen có chứa dòng “FASTA View” . Click vào vào mục 1 bắt đầu bằng ký hiệu NC_ sẽ hiện ra chuỗi của gene này dưới dạng file FASTA (hình). Vậy bước đầu thu thập khuôn mẫu đã hoàn thành trên cơ sở dữ liệu NCBI
Lưu ý: Như ở phần Graphics trên còn cung cấp cho chúng ta những đoạn gen theo chiều ngược lại (Gen mang màu đen). Vì vậy trước khi thực hiện thiết kế mồi, chúng ta cần phải đảo ngược đoạn khuôn mẫu này lại cho đúng chiều 5’-3’.
1.2. Thiết kế đoạn mồi
Bước 1: Truy cập trang chủ của phần mềm Primer-BLAST tại địa chỉ:http://www.ncbi.nlm.nih.gov/tools/primer-blast/. Giao diện chính của Primer-BLAST như hình.
(1) Khung nhập dữ liệu chuỗi khuôn mẫu: Nhập chuỗi dưới dạng file FASTA
(2) Thông số về nhiệt độ nóng chảy (Tm )của đoạn mồi : điều chỉnh giống với thông số của nguyên tắc thiết kế mồi ở phần 1 của loạt bài viết về thiết kế mồi cho phản ứng PCR
Ngoài ra còn rất nhiều các thông số nâng cao khác nhưng ở bài này chúng ta sẽ chỉ đi về mặt cơ bản. Vì thế hầu hết các thông số sẽ ở dạng mặc định.
Bước 2: Đánh giấu bỏ dòng “Enable search for primer pairs specific to the intended PCR template” để bỏ qua việc tìm kiếm cặp mồi có sẵn trong cơ sở dữ liệu của NCBI. Sau đó chúng ta thu về thiết kế primer bằng cách ấn vào ô “Get Primers”.
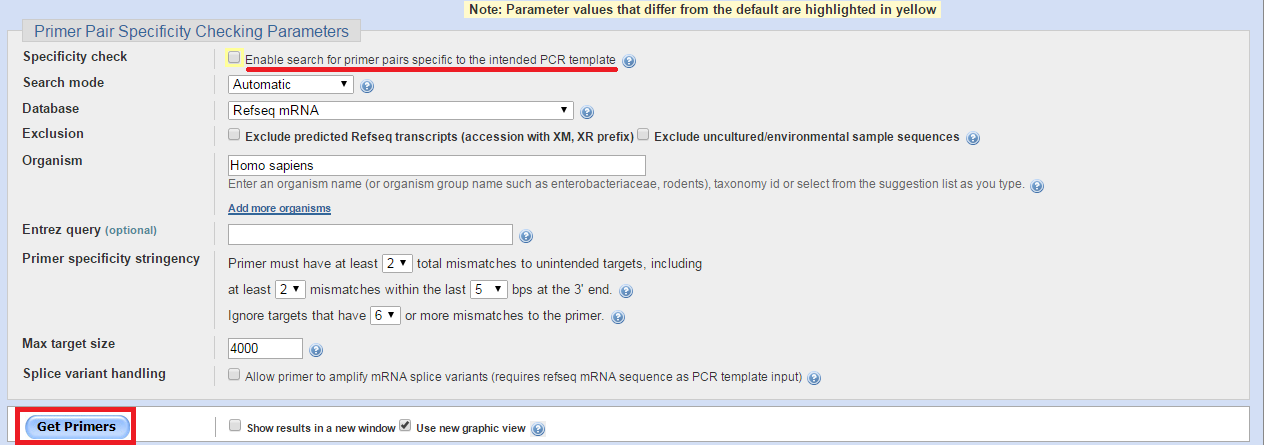
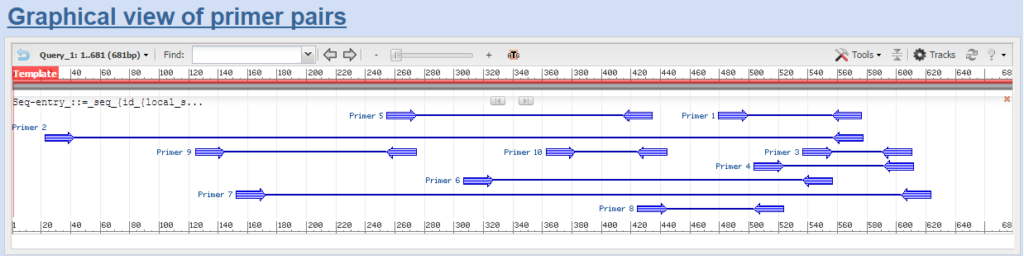
Cuối cùng, kết quả đoạn mồi thu được sẽ ở 2 dạng: hình ảnh trực quan và thông tin chi tiết về kết quả.

Đánh giá các phần mềm phổ biến hiện nay
- Phần mềm FastPCR là công cụ tích hợp hàng loạt các tính năng toàn diện và chuyên nghiệp dùng để thiết kế mọi loại mồi cho PCR. Mặc dù vậy, điểm yếu của phần mềm này là sự quá phức tạp khi sử dụng.
- Primer-BLAST là một phần mềm online được cung cấp bởi The National Center for Biotechnology Information (NCBI). Phần mềm này được tạo nên nhờ sự kết hợp giữa Primer3 và BLAST. Nổi trội nhờ khả năng sử dụng cơ sở dữ liệu lớn của NCBI bằng BLAST nhưng là một công cụ online, Primer-BLAST không tránh khỏi những hạn chế.
- Primer3 là một phần mềm mã nguồn mở cực kỳ nổi tiếng và BatchPrimer3 là bản phát triển sau này. Đặc điểm nổi bật của BatchPrimer là việc chạy trên nền web online và khả năng chạy thông lượng lớn đầu vào giúp BatchPrimer3 là một trong những công cụ phổ biến trong thiết kế mồi cho PCR nhằm thay thế cho người anh Primer3.
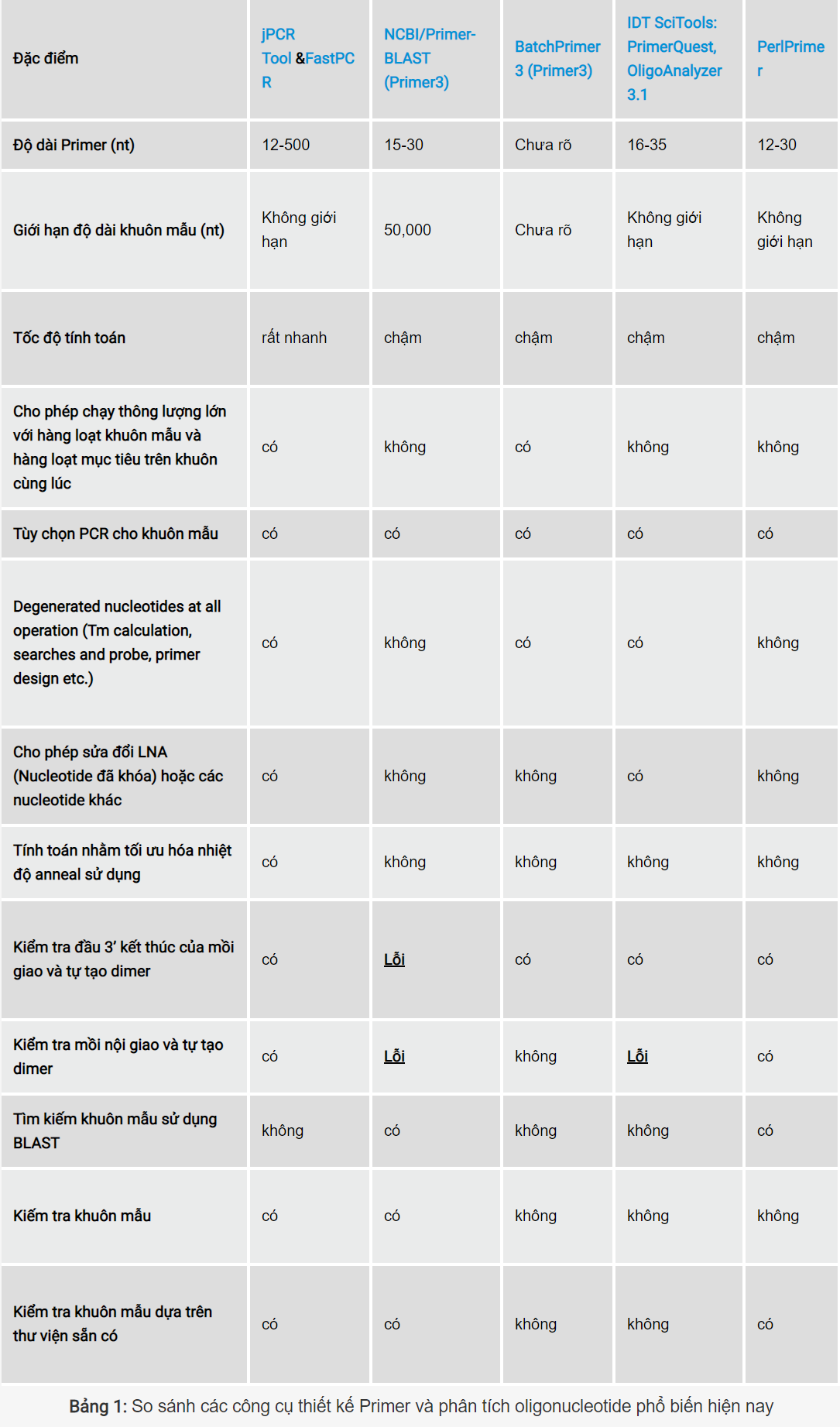
Ghi chú: Bảng so sánh trên mang tính chất tương đối vì do công ty cung cấp phần mềm jPCR Tool &FastPCR thống kê, vì thế khả năng các đặc điểm mang tính chất có lợi hơn so với các công cụ khác. Mặc dù vậy, đây là tài liệu đáng để tham khảo.
Tham khảo:
- PCR Primer Design Guidelines. PREMIER Biosoft.
- PrimerDigital.
Nguồn: IBSG Academic





