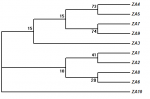
Chào các anh chị và các bạn, hiện em đang làm nghiên cứu về đa dạng di truyền cây thuốc. Sau khi giải trình tự nucleotide và phân tích các trình tự đó cần xây dựng cây phả hệ.Em đã dựng cây phả hệ (có đính kèm) bằng một số phần mềm như MEGA 5, BioEdit, CLC Sequence Viewer, ClustalX 2 tuy nhiên kết có cho ra giá trị hệ số Bootstrap thấp (<50%). Em muốn hỏi anh chị về những trường hợp này mình có nên sử dụng kết quả này và vì sao? Bên cạnh đó em được biết phần mềm PAUP 4.0* là phần mềm "mạnh" dùng để dựng cây phân loại vậy anh chị nào có thể giúp em tìm hoặc chia sẻ với em phần mềm này được thì tốt quá! Em cảm ơn anh chị rất nhiều!
Navigation
Install the app
How to install the app on iOS
Follow along with the video below to see how to install our site as a web app on your home screen.
Note: This feature currently requires accessing the site using the built-in Safari browser.
More options
You are using an out of date browser. It may not display this or other websites correctly.
You should upgrade or use an alternative browser.
You should upgrade or use an alternative browser.
Hỏi về phần mềm paup 4.0* và hệ số bootstrap
- Thread starter pvcfyt
- Start date
Similar threads
- Replies
- 0
- Views
- 3K
- Sticky
- Replies
- 44
- Views
- 38K
- Replies
- 13
- Views
- 11K